Bien que le choléra semble être une maladie du passé, il est encore aujourd’hui un grave problème de santé publique dans de nombreuses régions du monde, infectant chaque année de 1,3 à 4 millions de personnes et causant plus de 100 000 décès. L’émergence et la dispersion mondiale de cette maladie ont été bien documentées depuis l’apparition des premiers cas en Europe voilà de cela deux siècles. Même si des traitements existent, la menace ne cesse d’augmenter dans les pays où l’accès à l’eau potable est difficile. Dans les deux dernières décennies, la recherche fondamentale a cependant mené à une meilleure compréhension de la bactérie à l’origine du choléra, ce qui a permis le développement de nouveaux moyens de lutte contre cette maladie ancienne.
Le risque de contracter la maladie concernerait près de 1,3 milliard de personnes dans environ 70 pays où le choléra est considéré comme endémique *, selon l’Organisation mondiale de la santé (OMS) [1]. Le choléra est causé par Vibrio cholerae, une bactérie en forme de virgule naturellement présente dans l’environnement aquatique. Ingéré par l’entremise d’eau ou d’aliments contaminés, cet agent pathogène * colonise le système digestif humain et, une fois arrivé dans l’intestin, se multiplie et émet une toxine si virulente qu’elle amplifie de manière impressionnante la perte d’eau au niveau du système digestif, causant des vomissements et des diarrhées pouvant aller jusqu’à 15 litres par jour [2].
Cette perte donne aux victimes un teint cendré, leurs yeux s’enfoncent dans leurs orbites, leur sang s’assombrit et se fige dans les vaisseaux sanguins. La déshydratation sévère finit par entraîner la défaillance des organes et la mort, parfois quelques heures seulement après les premières crampes intestinales. En l’absence de traitement, entre un tiers et la moitié des cas s’avèrent fatals [3]. La bactérie se retrouve dans les selles de la personne infectée et peut se propager à d’autres individus en contaminant l’eau ou des aliments. Le choléra est ainsi une maladie extrêmement contagieuse, en particulier dans les régions où les eaux usées ne sont pas adéquatement traitées.
Les catastrophes naturelles ou provoquées par l’homme, les conflits armés et les déplacements de populations dans des camps de réfugiés surpeuplés représentent les facteurs de risque liés aux épidémies [4]. Les deux grosses épidémies actuelles en sont le parfait exemple. Le 12 janvier 2010, Haïti est frappée par un violent séisme qui prive de logement près d’un million d’habitants et qui détruit une grande partie des infrastructures du pays. Dix mois plus tard se déclare une épidémie de choléra dont le bilan se chiffre à près de 10 000 décès et à plus de 800 000 cas estimés en mai 2017 [5].
En proie à une épidémie de choléra pour d’autres raisons, le Yémen affiche aujourd’hui un bilan tout aussi lourd. Depuis 2015, ce pays est déchiré par une guerre causant une des plus grandes crises alimentaires du monde, ainsi que l’effondrement des structures médicales et sanitaires. Depuis avril 2017, il est également frappé par une épidémie de choléra à l’origine de plus de 500 000 cas et de près de 2 000 décès en seulement 4 mois [6].
Les origines de la « peur bleue »
Selon de nombreux récits, le choléra existerait en Inde et dans les pays limitrophes depuis l’Antiquité, mais la première pandémie de choléra a lieu en 1817, se répandant à partir des mangroves du golfe du Bengale. Lorsque la Compagnie britannique des Indes orientales envoie des milliers d’ouvriers dans les Sundarbans du delta du Gange pour étendre son empire commercial, elle n’est pas consciente de la dangerosité de ces eaux chaudes et saumâtres, berceau de la bactérie Vibrio cholerae [7].
À partir de son foyer asiatique, la maladie suit les voies du commerce et arrive sur d’autres continents. Elle gagne en février 1832 une Grande-Bretagne en pleine industrialisation, tuant plus de 7 000 personnes. Un mois plus tard, les premiers cas de la maladie se déclarent à Paris, où elle fera plus de 19 000 victimes. Elle y marquera tellement les esprits qu’un néologisme, inspiré du teint cyanosé du malade, en est issu, celui de « peur bleue [8] ».
La même année, une expédition transatlantique transporte les premières personnes atteintes du choléra en Amérique du Nord à Montréal et dans la ville de Québec, et 3 000 morts sont déclarés en aussi peu que 11 jours. Elle se répand par la suite aux États-Unis et frappe New York lors de l’été 1832, où elle tue, au pic de l’épidémie, plus de cent individus par jour [9]. En seulement un siècle, six pandémies se succèdent ainsi, faisant plusieurs dizaines de millions de victimes à travers le monde. La septième et actuelle pandémie débute en Indonésie en 1961, atteint l’Afrique en 1971, l’Amérique latine en 1991, puis plus récemment Haïti en 2010.
Une bactérie en forme de virgule
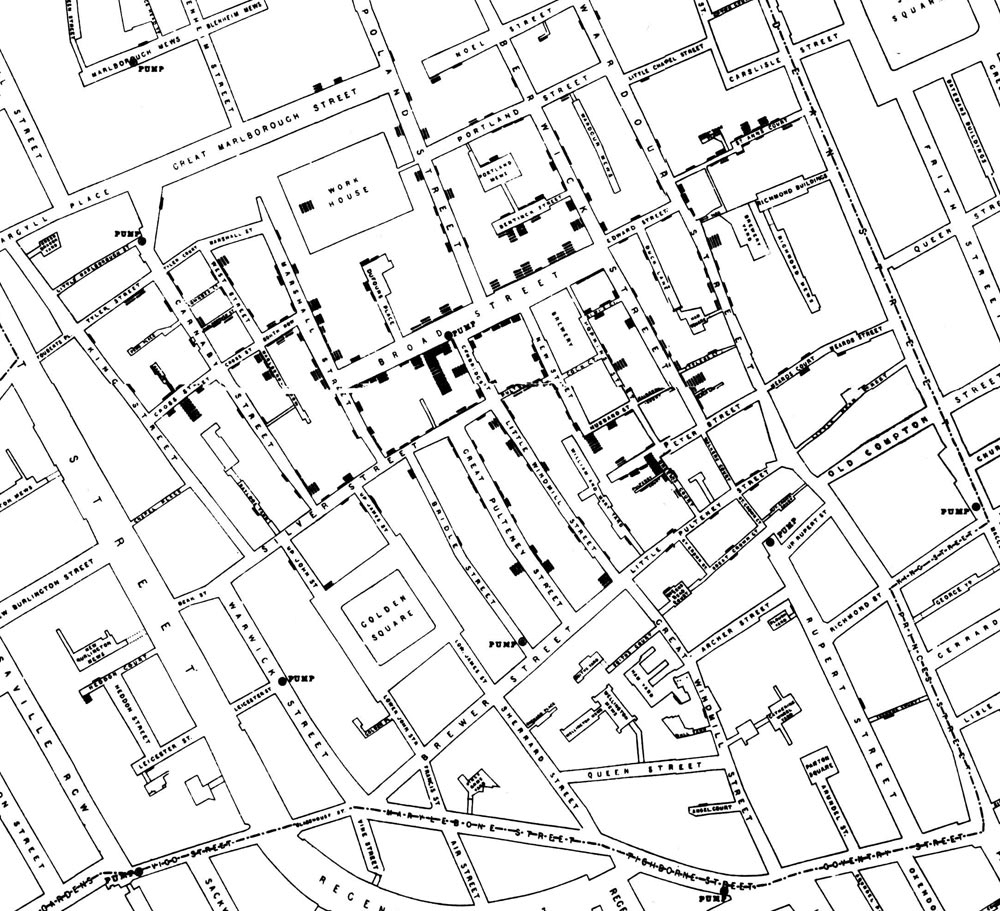
Dès les premières flambées de choléra en Europe, les scientifiques ont tenté de comprendre ses origines et son mode de transmission. Cependant, les premières découvertes permettant de lutter contre la maladie ne se font qu’à partir de la deuxième moitié du xixe siècle. En 1849, le médecin John Snow, père de l’épidémiologie moderne, soupçonne que la maladie se propage à travers le réseau de distribution des eaux [10]. Ainsi, en 1854, alors qu’une épidémie de choléra fait rage à Londres dans le quartier de Soho, il procède à une cartographie des lieux de résidence ou de travail des 578 victimes. Il remarque alors que le nombre de décès augmente progressivement à l’approche d’une pompe à eau publique : il détermine ainsi la source de la contamination. Fait intéressant, juste à côté de la fameuse pompe se trouvait une brasserie ne comptant aucune victime : les travailleurs ayant droit tous les jours à une ration de bière gratuite, ils n’avaient pas besoin de boire de l’eau de la pompe (voir la figure 1).
Légende : Épidémie de choléra de Broad Street (1854) par John Snow. Chaque rectangle noir représente un cas de choléra.
Source : Cheffins, C. F. (1854). Lith, Southampton Buildings, Londres (Angleterre). Dans J. Snow (1855). On the Mode of Communication of Cholera (2e éd.). Londres, R.-U. : John Churchill, New Burlington Street.
La même année, l’anatomiste italien Filippo Pacini isole et observe le bacille * cholérique pour la première fois. Pourtant, trente ans plus tard, Robert Koch, le célèbre médecin allemand découvreur du bacille tuberculeux, s’attire tout le mérite lié à cette avancée en révélant que Vibrio cholerae est la cause de la maladie. Un siècle plus tard, dans les années 1960, les biologistes indiens Sambhu Nath De et Nirmar Kumar Dutta démontrent que le bacille produit une puissante toxine [11].
Les traitements par réhydratation, conjointement avec l’administration d’antibiotiques, ont fait du choléra une maladie traitable, avec un faible taux de mortalité dans des conditions médicales appropriées [12]. Malgré cela, la présence persistante de la bactérie dans l’environnement [13] rend son éradication peu envisageable. Et même si Vibrio cholerae reste une des bactéries les mieux connues à ce jour, elle doit encore être surveillée, car elle se révèle être un agent pathogène ayant de grandes capacités à évoluer, et en particulier à acquérir une virulence plus importante ou une meilleure résistance aux antibiotiques.
Une meilleure compréhension de son ennemi
Les connaissances actuelles sur l’évolution de la bactérie Vibrio cholerae, et sur sa façon de devenir plus virulente et plus résistante aux antibiotiques, sur sa manière de s’adapter à de nouveaux environnements et de causer des épidémies dans des régions intouchées du monde doivent beaucoup aux récents développements des techniques de séquençage de l’ADN et aux avancées dans le domaine de la génomique bactérienne * [14]. Jusqu’à maintenant, les techniques d’analyse classiques en génétique, se focalisant uniquement sur une petite partie de la séquence d’ADN, donnaient une information très limitée et ne permettaient pas de voir de différences entre des bactéries très proches [15]. Le séquençage de génomes * entiers et leur comparaison ont notamment permis de constater ce qui différenciait des souches causant la maladie d’autres souches de Vibrio cholerae inoffensives pour l’homme [16]. En effet, ces dernières ne possèdent pas certains facteurs de virulence, tels que le pilus * TCP, qui permet à la bactérie de coloniser l’intestin, et le bactériophage * CTX. Celui-ci est un parasite astucieux qui a intégré l’ensemble de son génome dans celui de la bactérie afin de se multiplier avec elle, et qui en « échange » lui confère la capacité de produire la toxine cholérique [17]. Cependant, l’événement ayant permis à une bactérie aquatique au départ inoffensive de devenir un des tueurs les plus craints dans le monde pendant plus d’un siècle reste toujours un mystère [18].
L’étude des génomes de souches émergentes peut se révéler utile dans l’évaluation de l’efficacité des vaccins et dans l’amélioration de leur conception [19]. En effet, deux vaccins oraux sont actuellement disponibles et recommandés par l’OMS. Cependant, tous deux présentent une efficacité limitée à quelques années, et les raisons exactes de ce seuil sont inconnues. De plus, ils nécessitent une prise en deux temps, ce qui pose un problème logistique dans les régions où ils sont le plus indispensables [20].
Une menace de plus en plus inquiétante
La génomique bactérienne est aussi de plus en plus utilisée en épidémiologie pour retracer l’origine et le parcours des épidémies. Celle de choléra ayant débuté à Haïti en 2010 offre un bon exemple d’une telle application. En janvier 2010, un séisme de magnitude 7 frappait Haïti, détruisant une grande partie des infrastructures du pays et privant de logement plus d’un million d’Haïtiens. Dix mois plus tard, des soldats népalais débarquaient de Katmandou, où sévissait alors une épidémie de choléra, pour une rotation de six mois comme Casques bleus des Nations unies. Ils installèrent leur camp au-dessus de l’Artibonite, la plus grande rivière du pays. Les habitants remarquèrent rapidement que des eaux usées non traitées étaient évacuées du camp par un ruisseau affluent de l’Artibonite. Peu de jours après l’arrivée de ces soldats, le vibrion cholérique était ainsi introduit dans les eaux haïtiennes [21], et c’était le début de l’une des pires épidémies de choléra de l’histoire.
Plusieurs groupes de recherche internationaux tentent alors de déterminer l’origine, au départ inconnue, de cette épidémie, qui touchait une région n’ayant pas vu de cas de choléra depuis plus d’un siècle. Les premiers tests comparant les souches de choléra haïtiennes avec des souches d’Amérique latine, provenant d’épidémies ayant eu lieu au Mexique, au Brésil et au Pérou à partir des années 1990, révèlent de fortes différences entre les génomes des souches d’Haïti et celles du reste de l’Amérique latine. Les experts soupçonnent par la suite une origine asiatique de la maladie, les souches asiatiques étant plus proches génétiquement de celles haïtiennes. Finalement, en 2011, des chercheurs de plusieurs universités publient une étude comparant les séquences ADN de 24 souches népalaises avec des séquences de 10 souches haïtiennes, et montrent qu’elles sont quasi identiques, ce qui indique une origine népalaise de la maladie [22]. Un panel d’experts mandaté par l’ONU et plusieurs chercheurs indépendants arrivent rapidement à la même conclusion [23]. L’ONU a fini par reconnaître sa responsabilité dans l’origine de l’épidémie en août 2016.
Le choléra reste une menace pour la santé publique à l’échelle mondiale, ainsi qu’un indicateur de l’absence d’équité sociale et de l’insuffisance du développement social. L’approvisionnement en eau potable, l’assainissement des eaux usées et le traitement des matières fécales sont des conditions essentielles pour éradiquer la maladie dans les régions touchées. L’eau demeure cependant une ressource limitée dans beaucoup de pays, et près de 1,8 milliard de personnes consomment régulièrement de l’eau contaminée par des matières fécales [24]. De plus, une équipe de chercheurs de l’Université du Maryland a montré que le réchauffement climatique pourrait être un facteur supplémentaire pour le risque d’épidémies. En effet, en plus d’accroître les risques de catastrophes naturelles menant à une destruction des infrastructures (ouragans ou inondations comme celles observées durant l’été 2017 en Asie du Sud), la hausse de la température des océans favorise la multiplication des vibrions, et les infections augmentent [25].
Des actions de lutte prometteuses
Un des objectifs pour les années à venir dans la lutte contre cette maladie est l’amélioration de la vaccination [26]. De nombreuses équipes de recherche, comme celles basées au Centre international pour la recherche sur les maladies diarrhéiques, au Bangladesh, se concentrent sur le développement d’un vaccin donnant une protection plus longue dans le temps, et pouvant être administré en une seule dose, afin de diminuer tous les efforts logistiques nécessaires à son administration. Une autre approche dans la lutte contre les épidémies est l’amélioration des méthodes de diagnostic et de surveillance. En effet, lors d’une épidémie, beaucoup de personnes infectées par la bactérie ne présentent pas de symptômes. Dans les régions du monde où le choléra frappe de façon régulière, le nombre de porteurs sains est considérablement plus important que celui de malades (de 40 à 80 % des individus infectés), et leur rôle dans la transmission de l’agent pathogène de même que les causes de leur résistance sont encore mal connus [27]. Ainsi, le développement de nouveaux tests de diagnostic rapide et une meilleure compréhension du rôle des porteurs sains grâce à la recherche fondamentale permettraient d’améliorer la prévention et la prise en charge des épidémies.
Lexique
Bacille : bactérie en forme allongée dite « en bâtonnet », par opposition à la forme coccus (« ronde »).
Bactériophage : virus n’infectant que les bactéries.
Endémique : se dit d’une maladie qui est persistante dans une région.
Génome : ensemble des gènes d’un organisme, inscrit dans son ADN ou ARN (pour certains virus).
Génomique bactérienne : science qui consiste à décrypter l’information contenue dans le génome des bactéries.
Pathogène : tout facteur capable d’engendrer une lésion ou de causer une maladie chez l’être humain, chez les animaux ou chez les plantes.
Pilus : expansion de la surface d’une bactérie lui permettant de s’attacher à une bactérie ou à un autre support.
Références
[1] Ali, M., Nelson, A. R., Lopez, A.L. et Sack, D. (2015). Updated global burden of cholera in endemic countries. PLoS Neglected Tropical Diseases, 9(6), e0003832. doi :10.1371/journal.pntd.0003832
[2] Harris, J. B., LaRocque, R. C., Qadri, F., Ryan E. T. et Calderwood, S. B. (2012). Cholera. Lancet, 379(9835), 2466-2476. doi :10.1016/S0140-6736(12)60436-X
[3] Ibid.
[4] Ibid.
[5] Organisation mondiale de la santé. (2017a). Epidemiological Update. Cholera. 4 May 2017. Repéré à http://reliefweb.int/sites/reliefweb.int/files/resources/2017-may-4-phe-epi-update-cholera.pdf
[6] Organisation mondiale de la santé. (2017b). Le choléra touche désormais 500 000 personnes au Yémen [Communiqué de presse]. Repéré à http://www.who.int/mediacentre/news/releases/2017/cholera-yemen-mark/fr/
[7] Shah, S. (2016). Pandemic: Tracking Contagions, from Cholera to Ebola and Beyond (1re éd.). New York, N. Y. : Sarah Crichton Books.
[8] Raulot, J.-Y. et Bourdelais, P. (1987). Histoire du choléra en France : une peur bleue, 1832 et 1854. Paris, France : Payot.
[9] Shah, op. cit.
[10] Snow, J. (1855). The Mode of Communication of Cholera (2e éd.). Londres, R.-U. : John Churchill.
[11] Nair, G. B. et Narain, J. P. (2010). From endotoxin to exotoxin: De’s rich legacy to cholera. Bulletin of the World Health Organization, 88(3), 237-240.
[12] Harris et al., op. cit.
[13] de Magny, G. C., Murtugudde, R., Sapiano, M. R., Nizam, A., Brown, C.W., Busalacchi, A. J., … Colwell, R. (2008). Environmental signatures associated with cholera epidemics. Proceedings of the National Academy of Sciences, 105, 17676-17681. doi : 10.1073/pnas.0809654105
[14] Robins, W. P. et Mekalanos, J. J. (2014). Genomic science in understanding cholera outbreaks and evolution of Vibrio cholerae as a human pathogen. Dans N. G. Balakrish et T. Yoshifumi (dir.), Cholera Outbreaks (p. 211-229). Berlin, Allemagne : Springer Berlin Heidelberg. doi : 10.1007/82_2014_366
[15] Robins et Mekalanos, op. cit.
[16] Shapiro, B. J., Levade, I., Kovacikova, G., Taylor, R. K. et Almagro-Moreno, S. (2016). Origins of pandemic Vibrio cholerae from environmental gene pools. Nature microbiology, 2, 16240. doi : 10.1038/nmicrobiol.2016.240
[17] Harris et al., op. cit.
[18] Shapiro et al., op. cit.
[19] Organisation mondiale de la santé. (2010). Vaccins anticholériques : note d’information de l’OMS. Relevé épidémiologique hebdomadaire, 85(13), 117-128. Repéré à http://www.who.int/wer/2010/wer8513.pdf?ua=1
[20] Ibid.
[21] Shah, op. cit.
[22] Hendriksen, R. S., Price, L. B., Schupp, J. M., Gillece, J. D., Kaas, R. S., Engelthaler, D. M., … Shrestha, S. D. (2011). Population genetics of Vibrio cholerae from Nepal in 2010: Evidence on the origin of the Haitian outbreak. mBio, 2(4), e00157-11. doi : 10.1128/mBio.00157-11
[23] Organisation des Nations unies. (2011). United Nation final report of the independent panel of experts on the cholera outbreak in Haiti. Repéré à http://www.un.org/News/dh/infocus/haiti/UN-cholera-report-final.pdf
[24] Organisation mondiale de la santé (2017a), op. cit.
[25] Vezzulli, L., Grande, C., Reid, P. C., Hélaouët, P., Edwards, M., Höfle, M. G., … Pruzzo, C. (2016). Climate influence on Vibrio and associated human diseases during the past half-century in the coastal North Atlantic. Proceedings of the National Academy of Sciences, E5062-E5071. doi : 10.1073/pnas.1609157113
[26] Organisation mondiale de la santé (2010), op. cit.
[27] Nelson, E. J., Harris, J. B., Morris Jr, J. G., Calderwood, S. B. et Camilli, A. (2009). Cholera transmission: The host, pathogen and bacteriophage dynamic. Nature Reviews. Microbiology, 7(10). doi : 10.1038/nrmicro2204


MERCI. Explications très complètes, très claires et à la portée du profane. Je viens de lire « Le Hussard sur le toit » de Jean Giono. J’ai eu envie de savoir où nous en sommes avec ce fléau qu’est le choléra. Cet article est très utile.